142
تمامی اطلاعات درباره ژنوم های ویروس کرونا ، سارس ، H1N1 و ابولا
منبع :شمارۀ 1235 نشریه پزشکی امروز
تجزیه و تحلیل ژنومی، ابزاری قدرتمند برای درک شیوع بیماری ویروسی میباشد. تعیین توالی نمونههای ویروسی در حال حاضر آسانتر و مقرون به صرفهتر از گذشته است و میتواند با ارائه وضوح سطح نوکلئوتید از عوامل بیماریزای ناشی از شیوع ، روشهای اپیدمیولوژیک را تکمیل نماید.
تجزیه و تحلیل ژنومی، ابزاری قدرتمند برای درک شیوع بیماری ویروسی میباشد. تعیین توالی نمونههای ویروسی در حال حاضر آسانتر و مقرون به صرفهتر از گذشته است و میتواند با ارائه وضوح سطح نوکلئوتید از عوامل بیماریزای ناشی از شیوع ، روشهای اپیدمیولوژیک را تکمیل نماید. هدف از ایجاد مقالۀ تشریح جزئیات پیرامون روشهایی است که دادههای ژنومی میتوانند در درک شیوع بیماریهای ویروسی به ما کمک نمایند ،تا بتوان به آمادگی لازم جهت مقابله با شیوع این گونه از بیماریها در آینده رسید.
◄ 19-COVID :
19- COVID ، این کرونا ویروس جدید که با شیوع پنومونی غیرعادی ویروسی در ووهان چین سبب ایجاد این همهگیری گردید. 19- COVID براساس ارتباط فیلوژنتیک و ساختارهای ژنومی خود به دستۀ بتاکروناویروسها (Betacoronavirus) تعلق دارد. بتاکروناویروسهای انسانی(2-SARS-CoV،SARS-CoV وMERS-CoV)علاوهبر شباهتهای بسیار ،تفاوتهایی نیز در ساختار ژنومیک و فنوتیپی خود دارند که میتوانند بر پاتوژنز (بیماری زایی) آن ها تأثیر بگذارند.
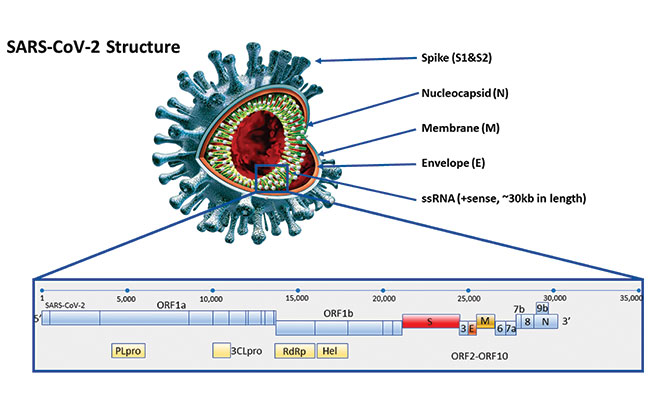
19- COVID دارای یکRNA تک رشتهای (سویمثبت) میباشد که با نوکلئوپروتئینی درون یک کپسید متشکل از پروتئین ماتریکس همراه است. یک CoV معمولی شامل حداقل شش ORF در ژنوم خود میباشد. تمامی پروتئینهای ساختاری و پروتئینهای لازم از sgRNAهای CoV ترجمه میگردند.چهار پروتئین ساختاری اصلی توسط ORFهای 10و 11 روی یکسوم ژنوم نزدیک انتهای Terminus- 3' رمزگذاری میشود. ساختار ژنتیکی و فنوتیپی 19- COVID در پاتوژنز از اهمیت برخوردار است. این مقاله در این بخش به مهمترین ویژگیهای کرونا ویروس در مقایسه با سایر بتاکروناویروسها میپردازد.
• ساختار ژنوم و چرخه زندگی ویروس کرونا:
19- COVID به صورت ذرات کروی یا چندشکلی است که دارای RNA تکرشتهای (سوی مثبت) همراه با نوکلئوپروتئین درون یک کپسید متشکل از پروتئین ماتریکس میباشد. پوشش (انولوپ) گلیکوپروتئینی این مجموعه را در بر میگیرد. برخی از کروناویروسها نیز حاوی پروتئین هِم(hem) آگلوتینین استراز (HE) هستند.
کروناویروسها دارای بزرگترین ژنوم (26.4 الی 31.7 kb) در میان تمام RNA ویروسهای شناخته شده ، با محتوای سیتوزین و گوانین از 32 تا 43 درصد متغیر هستند. تعداد متنوعی از ORF های کوچک میان ژنهای گوناگون حفظ شده (ORF1ab ، اسپایک ، انولوپ ، غشای و نوکلئوکپسید) در ردهبندیهای کروناویروس وجود دارد. ژنوم ویروسی شامل ویژگیهای متمایز ، از جمله قطعه منحصر به فرد N- ترمینال در پروتئین اسپایک است. ژن های اصلی پروتئینهای ساختاری در تمامی ویروسها به ترتیب 3’5’ به عنوان S ، E ، M و N رخ میدهند.
فراوانترین پروتئین ساختاری،گلیکوپروتئین غشایی(M) است. این پروتئین دو لایه غشا را تا سه بار پوشش داده و یک دامنۀ کوتاه NH2 ترمینال را در خارج از ویروس و یک دامنۀ طولانی COOH (دامنه سیتوپلاسمی) در داخل ویریون باقی میگذارد. پروتئین اسپایک (S) به عنوان گلیکوپروتئین غشایی نوع 1 پپلومر(1Membrane Glycoprotein Constitutes Peplomers) را تشکیل میدهد. در حقیقت،عامل اصلی خنثیسازی آنتیبادیها ، پروتئین S است. پروتئین M نقش مهمی در شکلگیری ذرات ویروسی داخل سلول، بدون نیاز به S دارد. در حضور تونیکامیایسین ، کرونا ویروس رشدنموده و ویروسهای بدون اسپایک که حاوی M بوده و بدون S هستند را تولید مینماید.
• فرآیند تکثیر کروناویروس در بیماری زایی:
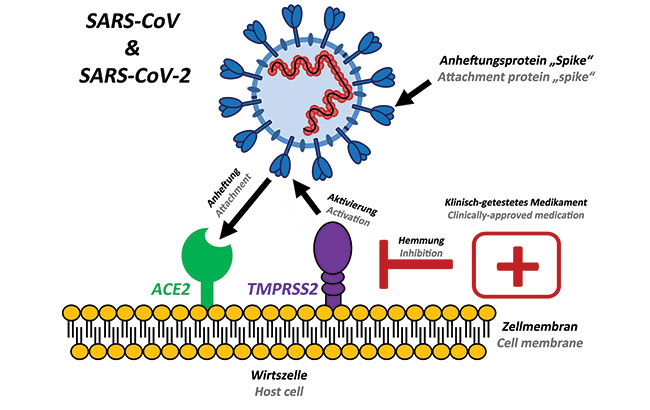
SARS-CoV-2 توسط اسپایک(Spike) به ACE2 (آنزیم تبدیل آنژیوتانسین 2 که یک نوع لیگاند سلولی است) متصل میشود و به 19- COVID اجازه میدهد تا وارد سلولها گشته و سبب را عفونت گردد. برای اینکه ویروس بتواند پس از این فرآیندهای نخستین، ورود به سلول را کامل نماید ، پروتئین اسپایک باید توسط آنزیمی به نام پروتئاز تحریک گردد. مشابه SARS-CoV-2، SARS-CoV ، برای تکمیل این فرآیند از پروتئازی به نام TMPRSS2 بهره میبرد. به منظور اتصال گیرنده ویروس (پروتئین اسپایک) به لیگاند سلولی آن (ACE2) ، فعال سازی توسط TMPRSS2 به عنوان پروتئاز مورد نیاز است.
پس از ورود ویروس به سلول میزبان پوشش آن از میان رفته ، ژنوم رونویسی و سپس ترجمه میشود. تکثیر و رونویسی ژنوم Coronavirus در سلول رخ داده و شامل فرآیندهای سنتز RNA مداوم و ناپیوسته است و همچنین در فرآیند ترجمه ماحصل یک مجموعه پروتئینی عظیم که توسط ژنی با 20 کیلو باز رمزگذاری شده است، میباشد. اعتقاد بر این است که این مجموعه پروتئینی با حداکثر 16 زیرواحد ویروسی و تعدادی پروتئین سلولی تشکیل شده است. پروتئینها در غشای سلولی جمع میشوند و RNA ژنومی به عنوان ذرات بالغ با جوانه زدن از غشای سلولی به خارج سلول ترشح میشوند.
• SARS-CoV:
تحلیل توالی ژنوم SARS-CoV (کرونا ویروس مرتبط با سندرم تنفسی حاد) برای درک تکامل و پاتوژنز این بیماری امری ضروری است. درمجموع ، 21 فریم خوانش باز (Open Reading Frame: ORFs) ژنها یا پروتئینهای غیرمشخص قلمدادشده (PUPs:Putative Uncharacterized Proteins) پیشبینی شدهاست. پیش از این هفت PUP گزارش نشده بود و پیش بینی میشد که دو مورد از آنها حاوی مناطق تراغشایی هستند.
هشت ORF به طور جزئی با ژنهای شناخته شده با یکدیگر تداخل دارند و نشانگر آن است که ژنوم SARS-CoV یک ژنوتیپ کوچک و کم حجم با مناطق کدگذاری شدهاست. جالبترین کشف این است که یک ORF در رشته منفی این ویروس قرار دارد. مناطق غیر کدشده و همچنین توالیهای تنظیم رونویسی (TRS:Transcription Regulating Sequences) در مناطق میان ژنتیکی شناسایی شدهاند.
کروناویروسها از اعضای خانواده ویروسهای انولوپدار (پوشش دار) هستند که در سیتوپلاسم سلولهای میزبان تکثیر میشوند. آن ها با حضور یک ژنوم RNA تک رشته سویمثبت ، طول حدود 30 کیلوباز که دارای یک ساختار 5’ capو 3 پلی آدنیلاسیون، متمایز میشوند. به محض آلوده شدن یک سلول میزبان مناسب ، قاب خوانش باز 5 (ORF) ژنوم ویروسی به یک پلی پروتئین بزرگ ترجمه میشود که توسط پروتئازهای کدشده ویروسی شکسته میشود تا چندین پروتئین غیرساختاری از جمله یک RNA پلی مراز وابسته به RNA و یک آدنوزین تریفسفاتاز (ATPase) هلیکاز آزاد شود.
این پروتئینها نیز به نوبه خود وظیفه تکثیر ژنوم ویروسی و همچنین رونوشتهای تو در تو را بر عهده دارند که در سنتز پروتئینهای ویروسی مورد استفاده قرار میگیرند.مکانیسم ساختهشده توسط این mRNAهای زیر ژنتیکی کاملا درک نشدهاست. با این حال ، شواهد اخیر نشان میدهد که توالی تنظیم رونویسی (TRS) در انتهای 5’ از هر ژن سیگنالهایی را تنظیم میکند که رونویسی ناپیوسته mRNA را تنظیم میکنند. TRS شامل توالی هستهای تا حدودی حفظ شده (CS) است که در برخی از ویروس ها به صورت 3’-CUAAAC-5’ میباشد.
پروتئینهای غشای ویروسی ، از جمله پروتئینهای اصلی S (اسپایک) و M (غشاء) ، وارد شبکه آندوپلاسمی (ER) میشوند در حالی که تمام طول تکرار شده RNA به علاوه رشتههایی مانند پروتئین N (نوکلئوکپسید) جمع میشوند. این مجموعۀ پروتئین RNA سپس با پروتئین M قرار گرفته در غشای ER ارتباط مییابد و ذرات ویروس به عنوان جوانههای پیچیده نوکلئوکپسید داخل لومن ER شکل میگیرند. سپس ویروس از طریق دستگاه گلژی مهاجرت میکند و سرانجام از سلول خارج میشود و روش به احتمال زیاد به دلیل اگزوسیتوز می باشد. محل اتصال ویروسی به سلول میزبان در پروتئین S ویروس قرار دارد.
◄ (2009 H1N1 Pandemic (H1N1pdm09 virus:
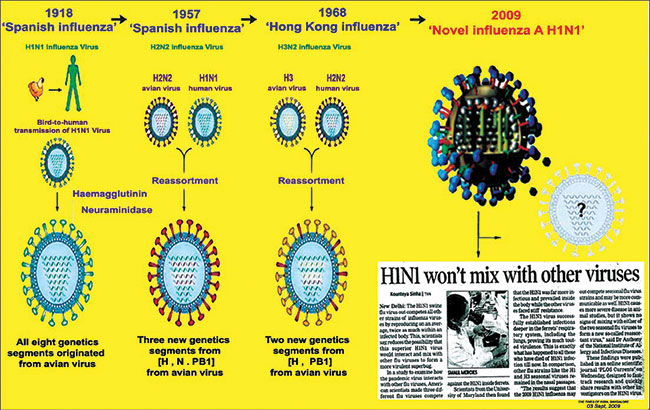
شیوع آنفلوآنزا به طور عمده در زمستان و در مناطق معتدل نیمکره شمالی و جنوبی رخ میدهد. با این حال ، شیوع آنفلوآنزا در مناطق گرمسیری اطراف استوا ممکن است در هر زمان از سال رخ دهد. آنفلوآنزا نه تنها سبب بیماریهای اپیدمی محلی سالانه میشود بلکه سبب همهگیریهای جهانی است. از قرن بیستم ، چهار بیماری آنفولانزا وجود داشته است: آنفلوآنزا H1N1 در سال 1918 ، آنفلوآنزا H2N2 در سال 1952 در آسیا ، آنفلوآنزا H3N2 در سال 1968 ، و آنفلوآنزا خوکی H1N1 در سال 2009. آنفلوآنزا H1N1 اسپانیا در سال 1918 ، که سبب کشتهشدن بیش از 50 میلیون نفر در سراسر جهان شد ، شدیدترین بیماری همهگیر و پاندمی جهان بود.
ویروس آنفلوآنزا یک بیماریزای تنفسی بسیار عفونی است و تهدیدی را برای سلامت عمومی جهانی رقم میزند. ویروس آنفلوآنزا A (H1N1) pdm09 ، که در سال 2009 پدیدار شد و سبب بروز همهگیری آنفلوآنزا جهانی شد ، اکنون یک ویروس آنفلوآنزا فصلی است که با آنفلوآنزا فصلی دیگری (H3N2) و ویروسهای آنفلوآنزا B همراه است. گستردگی ویروس A (H1N1) pdm09 در سراسر جهان نگرانیهایی پیرامون تنوع ژنوتیپی را افزایش میدهد که این تنوع قابلیت انتقال ویروس و بیماریزایی ویروس را افزایش داده و بر تولید واکسن اثر میگذارد.
• جداسازی ویروس :
نمونههای مثبت آنفلوآنزا A و B ، که از طریق آنالیز RT-PCR تشخیص دادهشدهبودند ، در سلولهایِ مخلوطِ کلیۀ سگ نژاد مادین- داربی (MDCK) تلقیح شدند تا ویروسهای آنفلوآنزا جدا شوند. سپس سلولهای کشت سلولی در 34 درجه سانتیگراد با 5 درصد CO2 انکوبه شدند و روزانه به مدت 5 روز این نمونهها کنترل میشوند تا اثر بیماریزایی را تشخیص دهند.
• توالی ژنوم :
ویروسهای آنفلوآنزا مدام در حال تغییر هستند. درحقیقت ، تمامی ویروسهای آنفلوآنزا با گذشت زمان دچار تغییرات ژنتیکی میشوند. ژنوم ویروس آنفلوآنزا شامل تمامی ژنهایی است که ویروس را تشکیل میدهند.
توالی ژنوم، توالی نوکلئوتیدها را در یک ژن نشان میدهد ، مانند حروف الفبا در کلمات. نوکلئوتیدها مولکولهای آلی هستند که واحد ساختاری اسیدهای نوکلئیک مانند RNA یا DNA را تشکیل میدهند. تمامی ویروسهای آنفلوآنزا از RNA تک رشتهای تشکیل شدهاست. ژنهای RNA ویروسهای آنفلوآنزا از زنجیرههای نوکلئوتیدها تشکیل شدهاند که به یکدیگر پیوسته شده و با حروف A ، C ، G و U کدگذاری شدهاند که به ترتیب در ترکیب آدنین ، سیتوزین ، گوانین و اوراسیل هستند. مقایسه ترکیب نوکلئوتیدها در یک ژن ویروس با ترتیب نوکلئوتیدها در یک ژن ویروس دیگر میتواند تغییرات میان این دو ویروس را نشان دهد.
تغییرات ژنتیکی بسیار مهم هستند زیرا میتوانند بر ساختار پروتئینهای سطح ویروس آنفلوآنزا اثر بگذارند. پروتئینها از توالی اسیدهای آمینه ساخته میشوند. تعویض یک آمینو اسید میتواند بر خواص ویروس تأثیر بگذارد، مانند انتقال ویروس میان افراد و میزان حساس بودن ویروس به داروهای ضدویروسی یا واکسن های فعلی.
ویروسهای آنفلوآنزا A و B ، ویروس های اصلی آنفلوآنزا که افراد را آلوده میکنند ، ویروسهای RNA هستند که هشت قطعه ژن دارند. این ژنها حاوی اطلاعاتی برای تولید ویروسهای جدید هستند و ویروس آنفلوآنزا پس از آلوده کردن یک سلول انسانی ، از یک فرد برای ترشح ویروسهای آنفلوآنزا استفاده مینماید و از این طریق سبب انتشار عفونت به سایر افراد میشود. ژنهای آنفلوآنزا دنبالهای از مولکولها به نام نوکلئوتیدها تشکیل شدهاند که به شکل زنجیرهای به هم متصل میشوند. این نوکلئوتیدها در ویروس آنفلوآنزا با حروف A ، C،G و U تعیین میشوند.
توالی ژنوم فرآیندی است که ترتیب یا دنباله نوکلئوتیدها (یعنی A ، C ، G وU) ژنهای موجود در ژنوم ویروس را تعیین میکند. توالی کامل ژنوم میتواند توالی تقریبا 13.500 حرفی از کل ژنوم ویروس را نشان دهد.
هر ساله CDC ترتیب توالی ژنوم را در حدود 7000 ویروس آنفلوآنزا از نمونههای بالینی اصلی جمع آوری شده از طریق نظارت ویروس را تحت بررسی قرار میدهد. ژنوم ویروس آنفلوآنزا A یا B شامل هشت بخش ژن است که 12 پروتئین ویروس را کد میکنند (یعنی ساختار و ویژگیهای آن را تعیین میکنند) ، از جمله دو پروتئین اولیه سطح آن، یعنی هماگلوتینین (HA) و نورآمینیداز (NA). پروتئینهای سطحی ویروس آنفلوآنزا ویژگیهای مهم ویروس را تعیین میکنند ، از جمله شیوۀ پاسخ ویروس به برخی داروهای ضدویروسی ، تشابه ژنتیکی ویروس به ویروسهای واکسن آنفلوآنزا فعلی و پتانسیل ویروسهای آنفلوآنزا زونوتیک (منشأ حیوانی) برای آلوده نمودن میزبان های انسانی.
• خصوصیات ژنتیکی :
CDC و سایر آزمایشگاههای بهداشت عمومی در سراسر جهان ژنهای ویروسهای آنفلوآنزا را از دهه 1980 دنبال میکنند. CDC از ویژگیهای ژنتیکی به دلایل زیر استفاده میکند:
• تعیین میزان ویروسهای آنفلوآنزا مرتبط یا مشابه آنها از نظر ژنتیکی با یکدیگر
• جهت نظارت بر شیوۀ تکامل ویروسهای آنفلوآنزا
• شناسایی تغییرات ژنتیکی که بر ویژگیهای ویروس تأثیر میگذارد. به عنوان نمونه ، جهت شناسایی تغییرات خاص که با ویروسهای آنفلوآنزا همراه هستند و آسانتر شیوع پیدا میکنند، سبب بیماری شدیدتر میشوند یا مقاومت در برابر داروهای ضد ویروسی ایجاد میشود.
• ارزیابی واکسنهای آنفلوآنزا در برابر ویروس آنفلوآنزای خاص براساس شباهت ژنتیکی آن به ویروس
• نظارت بر تغییرات ژنتیکی ویروسهای آنفلوآنزا در جمعیتهای حیوانات که می توانند سبب آلودهشدن انسان شوند.
تفاوتهای نسبی میان گروههای ویروسهای آنفلوآنزا با سازماندهی آنها در گرافیکی به نام "درخت فیلوژنتیک" نشان داده شدهاست. درختوارۀ فیلوژنتیک برای ویروسهای آنفلوآنزا مانند شجرهنامه خانوادگی(تبارشناسی) برای افراد میباشد. این درختوارهها نشان میدهند که ویروسهای فردی با چه ارتباطی نزدیک به یکدیگر هستند. براساس اینکه نوکلئوتیدهای ژن آنها یکسان هستند یا خیر ، ویروسها با هم گروه بندی میشوند.
درختان فیلوژنتیک ویروسهای آنفلوآنزا اغلب نشان میدهند که ژنهای هماگلوتینین (HA) یا نورآمینیداز (NA) ویروسها با یکدیگر چقدر مشابه هستند. هر دنباله از ویروس آنفلوآنزای خاص ، شاخۀ خاص خود را بر روی درختواره دارد.
CDC ویژگیهای ژنتیکی ویروسهای آنفلوآنزا را در تمام طول سال جمع آوری میکند. این دادههای ژنتیکی در رابطه با دادههای توصیفی آنتیژن ویروس جمع آوری میشوند تا به تعیین اینکه کدام ویروس واکسن باید برای واکسنهای آنفلوآنزا نیمکرۀ شمالی یا نیمکرۀ جنوبی آینده انتخاب شود ، استفاده میشود.
توالی ژن HA و NA ویروسهای فعلی میتوانند به عنوان واکسنی در برابر ویروسهای آنفلوآنزا باشد. از آنجا که ویروسهای جمعآوری شده ، از نظر ژنتیکی مشخص میشوند ، تفاوتها آشکار است. در طول یک فصل ، این ویروسها از نظر ژنتیکی تغییر میکنند و سبب میگردد که واکسن مربوطه دیگر عمل نکند و نیاز به واکسن دیگری باشد. این موضوع نشانگر آن است که ممکن است ویروسِ واکسن دیگری برای واکسن فصل آنفلوآنزا بعدی انتخاب شود ، اگرچه سایر عوامل ، از جمله یافتههای خصوصیات آنتیژنیک ، به شدت بر تولید واکسن تأثیر میگذارند. پروتئینهای سطح ویروس آنفلوانزا HA و NA آنتی ژن هستند ، به این معنی که توسط سیستم ایمنی بدن شناخته میشوند و بدن قادر به ایجاد پاسخ ایمنی و قادر به تولید آنتیبادیهایی میشود که میتوانند عفونت را مسدود کنند. ویژگیهای آنتی ژن به تجزیه و تحلیل واکنش ویروس با آنتیبادیها اشاره میکند تا به ارزیابی شیوۀ ارتباط آن با ویروس دیگر کمک نماید.
• روشهای تعیین توالی ژنوم آنفلوآنزا:
دانشمندان در یک روش نه چندان جدید از یک روش تعیین توالی به نام "واکنش سانگر"(Sanger Reaction) برای نظارت بر تکامل آنفلوآنزا به عنوان بخشی از نظارت ویروس استفاده میکردند. توالی Sanger توالی ژنتیکی غالب ، در میان بسیاری از ویروسهای آنفلوآنزا میباشد. دانشمندان اغلب از روش Sanger جهت انجام توالی جزئی ژنوم ویروسهای آنفلوآنزا استفاده میکنند ، در حالی که فنآوریهای جدیدتر برای توالی کل ژنوم مناسبتر هستند.
در طی پنج سال گذشته ،CDC با استفاده از روش "Next Generation Sequencing ) NGS)"، که میزان اطلاعات و جزئیاتی را که تجزیه و تحلیل توالی ارائه میدهد ، به میزان زیادی گسترش داد. NGS از ردیابی مولکولی پیشرفته (AMD) برای شناسایی توالیهای ژن از هر ویروس در یک نمونه استفاده میکند. بنابراین ، NGS تغییرات ژنتیکی را میان بسیاری از ذرات ویروس آنفلوآنزای مختلف در یک نمونه واحد نشان میدهد ، و این روشها همچنین کل ناحیه کد شده ژنوم را نشان می دهد.
◄ ابولا:
ویروس ابولا ، یک ویروس RNA تک رشتهای ، سوی منفی و به صورت ژنوم کوچک است. یک شاخه از ویروس ابولا سبب شیوع اخیر آن در غرب آفریقا گردید. ویروسهای ابولا به خانواده فیلوویریده تعلق دارند و به همراه پارامیکسوویریده ، رابدوویریده و ویروس بیماری Borna ، ویروسهای فیلوویریده متعلق به mononegavirales هستند. ژنوم ویروس ابولا مانند تمام ژنوم فیلوویریدهها مشابه ژنوم ویروس ماربورگ است. فیلوویریده میتواند سبب تب و خونریزی شدید در پستانداران و همچنین در انسان شود.
Mononegavirales اصطلاحی است که برای "ویروسهای RNA دار سوی منفی nonsegmented) NNSV)" استفاده میشود. این ویروسها انولوپدار (پوششدار) هستند که مینی ژنومها متشکل از یک مولکول RNA منفرد با سو منفی یا مکمل mRNA هستند. از این رو ژنوم ویروس ابولا و همچنین تمام ژنومهای آنتی ویروس به عنوان ژنوم کوچک در نظر گرفته میشوند. به نظر میرسد ژنوم سنتز شده ویروس ابولا بدون پروتئین ، فاقد خاصیت بیماریزایی است.
اسیدهای نوکلئیک جدا شده از ویروسهای RNA منفی یا سلولهای آلوده به ویروس نمیتوانند یک چرخه عفونت را هنگام ورود به سلول میزبان آغاز کنند. از این معیار برای تمایز "مثبت" از ویروسهای RNA- "منفی" استفاده شده است. برای تولید mRNA ها ، ابتدا باید ژنوم ویروس رونویسی شود ، بنابراین ، ویروس RNA ویروس به طور خالص عفونی نیست ، ویروس باید RNA پلیمراز خود را وارد عمل کند. برای اینکه ویروس سلولی را آلوده کند ، یک پلیمراز ویروسی باید جزئی از ذرات ویروسی یا ویریون باشد.
ویژگی های ژنوم ویروس های RNA دار سوی منفی عبارتند از:
• RNA به صورت سنس منفی در ویریون می باشد.
• RNA پلیمراز حد واسط رونویسی و تکثیر می باشد.
• ژنوم به 6 mRNA جداگانه (از روی یک پروموتر) رونویسی می شود.
• تکثیر با سنتز یک آنتی ژن RNA کاملا مثبت انجام میشود.
• نوکلوپروتئین یک الگوی عملکردی برای سنتز mRNA است.
• نوکلوکپسیدهای ویروس با سطح سلول به طور مستقل اتصال مییابند.
• تکثیر آن ها عمدتا در سیتوپلاسم است.
• میتواند در بیمهرگان ، مهرهداران و گیاهان رخ دهند.
• بیماریزایی ویروس ابولا:
ویروس ابولا حاوی نوعی ماده ژنتیکی به نام RNA است که مشابه DNA است. برخلاف حیوانات و گیاهان،که از DNA به عنوان مخزن اطلاعات استفاده میکنند ، ویروس ها زنده نیستند زیرا بدون کمک سلول میزبان قادر به تکثیر نیستند. برای ایجاد ویروسهای جدید ، ویروس باید وارد یک سلول زنده شود ، محلی که اجزای سلول میزبان را ربوده تا اهداف خود را تحقق بخشد.
برای ورود به سلول ، ویروسِ ابولا باید از طریق غشای سلولی عبور نماید ، این سدی است که وظیفۀ محافظت از سلول را دارد. با این وجود ، تمام سلول ها به مواد مغذی احتیاج دارند که باید راههایی برای ورود به سلول داشته باشند. ویروسها از طریق یکی از این ورودیهای جذب مواد مغذی ، به داخل سلول وارد میشوند. ویروس ابولا از یک فرآیند غیر اختصاصی به نام ماکروپینوسیتوز استفاده مینماید ، که اجازه میدهد ویروس با یک حرکت موج مانند ، مانند بلعیدن وارد سلول شود.
بیشتر اعضای جنس ابولاویروس سبب بیماری شدید در انسان میشوند. در اینجا ، ما گزارش می دهیم که Ebolavirusها یک مکانیسم تکثیر ژنوم را تکامل دادهاند که آن ها را از سایر ویروس های NNS RNA متمایز میکند. استراتژی تکثیر Ebolavirus شامل اضافه کردن یک 3’نوکلئوتید نمونه برداری نشده در انتهای ژنوم است که ممکن است در جلوگیری از تشخیص ضدویروسی کمک کند.
بیشتر ژنوم های ویروس RNA سوی منفی (NNS) دارای نوکلئوتیدهای ترمینال 3’ و 5’ مکمل هستند زیرا پروموتورها در انتهای 3’ ژنومها و آنتی ژنومها تقریبا با یکدیگر یکسان هستند. با این حال ، با توجه به توالی منتشر شده ، هر دو انتهای ژنوم Ebolavirus نشان از درجه بالایی از تنوع و نوکلئوتیدهای ترمینال 3’ و 5’ مکمل نیستند. ترمینال 3’ متغیر است و اغلب 3’-GCCUGU ، ACCUGU یا CCUGU است.
◄ نتیجهگیری:
ژنوم ویروس به دلیل کوتاه بودن زمان تکثیر و ایجاد نسخههای متعددی از خود در سلول هدف ، بهعنوان یکی از ارگانیسمهای بسیار سریع در حال رشد در زیست شناسی در نظر گرفته میشود. ژنوم ویروس در درک بهتر ما از اپیدمیولوژی ، تشخیص ، نظارت و تکامل آنها ، نقش مهمی دارد. با توجه به اینکه ساختار اصلی ژنوم ویروس به خوبی محافظت میشود ، تعیین ژنوم در اکثر ویروسها ، درک بیماری زایی آنها و شناسایی ویروسهای جدید به راحتی انجام میشود. این توالی ژنوم در بانکهای اطلاعاتی مانند بانک ژن (GenBank) نگهداری میشود.











ثبت نظر